Domaine et contexte scientifiques: Certaines pathologies cardiaques ont un impact sur la mécanique du cœur et conduisent à une réduction de l’efficacité de sa fonction de pompe. Dans le contexte des pathologies ischémiques, nous cherchons à mieux diagnostiquer la présence et l’étendue d’un infarctus du myocarde à l’aide d’algorithmes d’analyse statistique et d’apprentissage appliqués sur les images acquises chez le patient [1]. Afin de valider ces algorithmes, nous développons des modèles numériques réalistes qui simulent la fonction cardiaque normale et pathologique [2] pour la constitution de grandes bases de données de modèles et d’images de synthèse (voir Figure ci-dessous). Ces modèles sont personnalisés sur les données de patients réels, c’est-à-dire qu’ils sont sensés reproduire au mieux la fonction cardiaque à partir d’une géométrie issue des données d’imagerie, et de paramètres adaptés. En se basant sur des données extraites d’images réelles (acquises en clinique), nous souhaitons augmenter le réalisme de ces modèles afin de mieux simuler la présence et les caractéristiques d’un infarctus du myocarde.
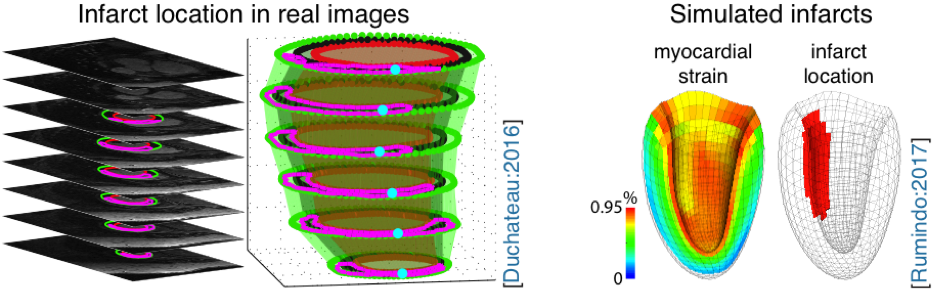
Figure : exemple d’une segmentation d’image de rehaussement tardif (rouge et vert : myocarde, rose : infarctus), et de simulation d’infarctus avec le modèle développé à CREATIS [2].
Objectif: Dans le cadre du stage proposé, nous visons les deux objectifs suivants:
- Caractériser statistiquement 3 aspects clés de l’infarctus à partir de données réelles déjà segmentées :
- La localisation et l’extension spatiale du territoire infarci (par rapport aux coronaires et à la transmuralité de la lésion) [4]
- le degré de viabilité des territoires infarcis et périphériques, traduit dans les paramètres du modèle
- les changements géométriques de la cavité (appelés remodelage [3-4])
- Intégrer ces caractéristiques dans les simulations actuellement effectuées, et étudier leur pertinence pour la validation des algorithmes de diagnostic de l’infarctus.
Méthodologie: La démarche d’analyse s’appuiera sur des données d’imagerie par rehaussement tardif, déjà segmentées. Il s’agira d’en extraire les paramètres géométriques et tissulaires pertinents (mesures spécifiques ou prise en compte de la totalité des segmentations) et de caractériser leur distribution statistique. Dans un deuxième temps, il s’agira d’élaborer une démarche pratique d’intégration de ces caractéristiques aux simulations numériques actuellement effectuées. Leur pertinence sera évaluée par rapport à des algorithmes de diagnostic existants.
Profil:
- Connaissances en analyse de données et traitement d’images
- Motivation spécifique pour le domaine médical
- Compétences en programmation (MATLAB, Python, ou C/C++)
Durée et indemnisation:
6 mois à partir de Février 2018, ~540€ / mois
Candidature :
Envoyer CV, lettre de motivation, et relevé de notes à : nicolas.duchateau@creatis.insa-lyon.fr
Bibliographie sur le sujet :
[1] Duchateau N, De Craene M, Allain P, Saloux E, Sermesant M. Infarct localization from myocardial deformation: Prediction and uncertainty quantification by regression from a low-dimensional space IEEE Transactions on Medical Imaging, 35:2340-52, 2016.
[2] Rumindo GK, Duchateau N, Croisille P, Ohayon J, Clarysse P Strain-based parameters for infarct localization: evaluation via a learning algorithm on a synthetic database of pathological hearts. Proc. International Conference on Functional Imaging and Modeling of the Heart (FIMH), LNCS, 10263:106-14, 2017.
[3] Sutton & Sharpe. Left ventricular remodeling after myocardial infarction: pathophysiology and therapy. Circulation, 101:2981-8, 2000.
[4] Richardson WJ, Clarke SA, Quinn TA, Holmes JW. Physiological implications of myocardial scar structure. Comprehensive Physiology, 5:1877-909, 2015.
