Verrou
Développements méthodologiques
Statistiques d’images US (D. Friboulet, O. Bernard Interaction avec l’équipe 3 Imagerie Ultrasonore)
Nous proposons le développement d'un modèle statistique basé sur les K-distributions, permettant la modélisation conjointe des régions sanguines et myocardiques et adapté à la segmentation. Le modèle des K-distributions a été développé initialement dans un objectif de caractérisation tissulaire pour des images échographiques enveloppe. L'application d'un tel modèle dans un cadre de segmentation pose un certain nombre de difficultés : d'une part la consistance des estimateurs des paramètres caractérisant la distribution n'est pas assurée dans la mesure où ces paramètres tendent vers l'infini pour les zones correspondant au sang; d'autre part la complexité de ce modèle rend difficile une implantation efficace pour une tâche de segmentation. Afin de pallier ces difficultés, nous proposons d'étendre le modèle des K-distributions à l'image échographique radiofréquence (RF). Les premiers résultats [BERN-06a, IEEE Trans Ultrason Ferroelectr Freq Control] [BERN-07, IEEE Trans Ultrason Ferroelectr Freq Control] montrent en effet que l'expression du modèle pour les données RF permet d'envisager une approximation efficace des K-distributions et le développement d'estimateurs plus stables.
Multimodality digital model of the thorax, heart and vessels (P. Clarysse, M. Orkisz, I. Magnin, D. Sarrut, Interaction with teams 2 Imagerie Volumique and 8 Imagerie morphologique et fonctionnelle)
Nous avons développé un modèle numérique du thorax respirant et du cœur battant [HADD-07, thèse], [HADD-05c, ITBM-RBM] (Figure 3). Ce modèle intègre une représentation de l’anatomie et du mouvement des différentes structures, les paramètres géométriques et fonctionnels associés et un ensemble d’images issues de la simulation d’acquisitions en différentes modalités, IRM (simulateur IRM SIMRI développé au laboratoire) et TEP (Simulateur TEP SORTEO, CERMEP, Lyon) notamment. Nous cherchons maintenant à inclure une variabilité de formes et de fonctions permettant ensuite de représenter une gamme d'anatomies personnalisées et de comportements normaux et pathologiques. D’autre part, de plus en plus de simulateurs d’images médicales devenant disponibles, une plateforme d’imagerie virtuelle multimodalités est en cours de développement [Sorina-08, MICCAI Workshop] dont un des principaux objectifs est de masquer la difficulté généralement rencontrée dans la mise en œuvre pratique de ces simulateurs. Il s’agit de reproduire dans un contexte de simulation le protocole clinique d’acquisition d’images dans diverses modalités.
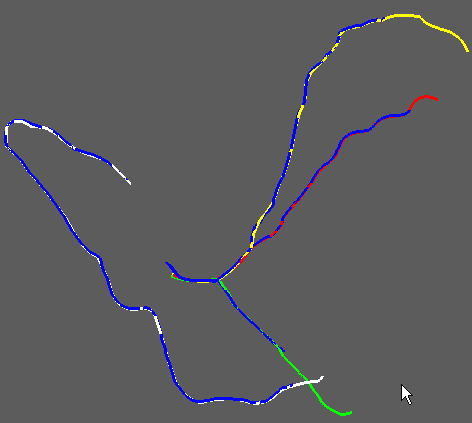
The thorax-heart model also has to include a representation of the coronary tree obtained from image segmentation. The segmentation of 3D arborescent structures, such as the coronary tree, requires a reliable detection of bifurcations, as well as a capability of distinguishing the end of a branch from an apprent discontinuity owing to a local narrowing. Nous privilégions l’approche locale multi-échelle avec suivi de la branche mère et détection récursive des bifurcations et des branches filles ORKI-08, Mach Graph Vision
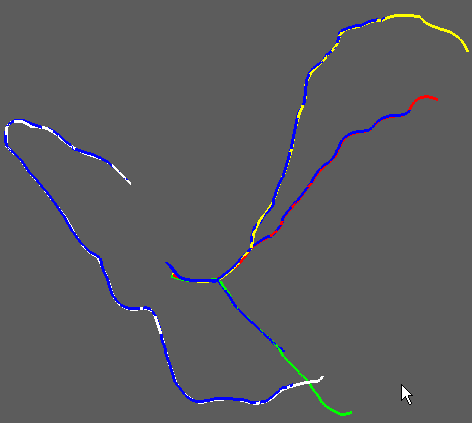
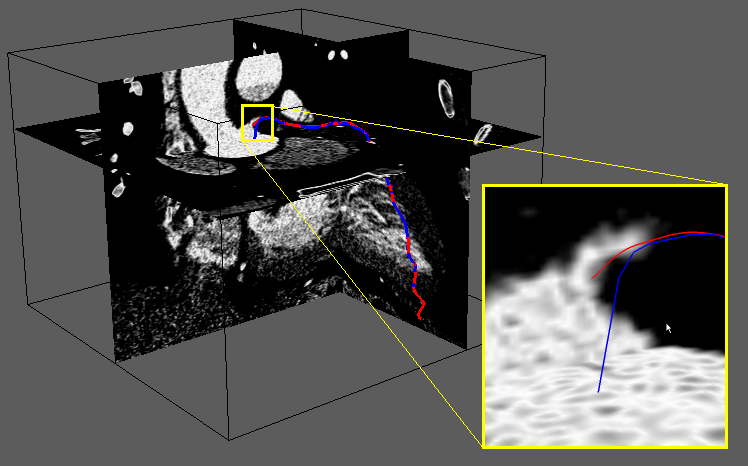
Extraction of coronary artery centerlines. Left: comparison between centerlines extracted starting from one click per artery (blue) and centerlines traced by experts (other colors), in four principale coronary branches (data from CAT'08 challenge). Right: details of the comparison in a right coronary artery.
En utilisant les modélisations a priori effectuées à partir des images TDM 4D (cf. section 2.1), nous avons pu proposer deux méthodes de reconstruction compensée en mouvement d'images Cone-Beam (une méthode analytique et une algébrique) [RIT-07, EMBC], [RIT-07, SPIE MI], [RIT-07, ICCR]. Ces méthodes permettent de reconstruire des images sans ou avec très peu d'artéfact de mouvement. D'autre part, un nouveau modèle d'estimation de mouvement directement à partir des projections Cone-Beam est proposé [VAND-08, MICCAI Workshop][VAND-07, ICCR]. Notons que, dans le cadre de ces travaux, un logiciel open-source (vv) a été développé et est proposé à la communauté [SERO-08, MICCAI Workshop].
Vascular digital simulation (G. Courbebaisse, M. Orkisz, Interaction with team 8 Imagerie morphologique et fonctionnelle)
Parmi les techniques utilisées en simulation numérique (éléments finis, méthodes particulaires) la méthode Lattice Boltzmann trouve des applications dans de nombreux domaines. Son adaptation pour la modélisation et la simulation organe ou modalité –dépendante est un challenge pour les prochaines années. Nous étudions sa mise en œuvre dans le cadre de la simulation d'écoulements viscoélastiques et plus spécifiquement de la thrombose dans les anévrismes. A priori, cette méthode qui prend en compte des grandeurs physiques à l’échelle microscopique pour simuler le comportement du système étudié à l’échelle macroscopique est adaptée aux systèmes multi-échelles auquel nous sommes confrontés. Ce travail de recherche s’appuie sur une collaboration entre le SPC (Scientific and Parallel Computing Group) de l'Université de Genève, le LIN (Laboratoire d’Ingénierie Numérique) de l’EPFL et CREATIS-LRMN [COUR-06b, MMM2006] et entre dans le cadre du projet européen COST P19. Les premiers résultats obtenus donnent une estimation du volume ‘thrombosé’ dans un anévrisme [MALA-08, Modern Physics], [NAVA-08, Computer Physics Communications]. A terme, l’objectif est de permettre un diagnostic patient spécifique pour détecter les anévrismes à risque qui nécessiteraient une intervention.
Par ailleurs, le modèle déformable simplexe de cylindre précédemment développé dans l’équipe a été exploité pour la simulation de la pose de stents artériels à partir d’une imagerie angiographique 3D FLOR-07b, ITBM
Simulation Monte-Carlo pour la dosimétrie (D. Sarrut, Interaction avec l’équipe 2 Imagerie Volumique)
Le premier objectif consiste à proposer des représentations d'images spatio-temporelles adaptées aux logiciels de simulation d'interaction rayonnement-matière par méthode Monte-Carlo afin d'en accélérer les temps de calcul tout en préservant le degré de précision requis par les médecins [AYAD-06, AAPM]. Pour des milieux de géométrie complexe et dynamique, cela nécessite l'étude de grilles irrégulières isothétiques et d'algorithmes de navigation de particules au sein d'environnements 3D/4D. Sur le versant dosimétrie, le but est d'obtenir une carte volumique de la dose reçue par patient (ou dose transmise dans le cas de la simulation d'un imageur portal) lors d'une irradiation thérapeutique lorsque le milieu est décrit par une géométrie complexe et dynamique (plusieurs millions de voxels).
Ce travail est intégré dans l’ANR « blanche » SIMCA2 (« SIMulation CAncer CArbone ») dont l’objectif est de proposer une plate-forme permettant de simuler le dépôt de dose issu d'une irradiation par faisceaux d'ions Carbone (Hadronthérapie) à l'intérieur d'un patient virtuel. Nous avons jusqu’ici proposé un algorithme de navigation permettant d'accélérer fortement (jusqu'à un facteur 15) les simulations de distribution de dépôt de dose effectuée avec le code Monte-Carlo Geant4 [SARR-08, Medical Physics]. Cette méthode repose sur une segmentation et une carte de distance adaptées au déplacement des particules simulées. Une partie de ce travail s’intègre également dans le cadre du projet régional d'hadronthérapie ETOILE.
Résultats